メタゲノム由来ゲノムを収集・整理した統合データベース 「Microbiome Datahub」を開発 ―21万ゲノム以上のMAG配列と環境・機能情報を統合し、微生物研究を加速―
公開日:2026年3月30日
本研究成果は、2026年3月16日に科学誌「Microbiome」に速報版が掲載されました。
京都大学化学研究所 松井求 助教、情報・システム研究機構国立遺伝学研究所 森宙史 准教授、自然科学研究機構基礎生物学研究所 内山郁夫 准教授、東京科学大学生命理工学院 山田拓司 教授を中心とする共同研究グループ(京都大学、国立遺伝学研究所、基礎生物学研究所、東京科学大学、東京大学)は、環境中の微生物を解析したメタゲノム由来のゲノム配列(MAG: Metagenome-Assembled Genomes)を公共の塩基配列リポジトリから網羅的に収集し、環境や系統・遺伝子機能等、様々な情報を付加した統合データベース「Microbiome Datahub」を開発・公開しました。本データベースは、公共の塩基配列リポジトリに蓄積された21万件以上のMAG配列に対し、統一された遺伝子予測、系統分類、遺伝子機能アノテーション、表現型予測および環境メタデータを付与したものであり、データ駆動型の微生物学や未知の有用タンパク質探索の基盤として貢献することが期待されます。
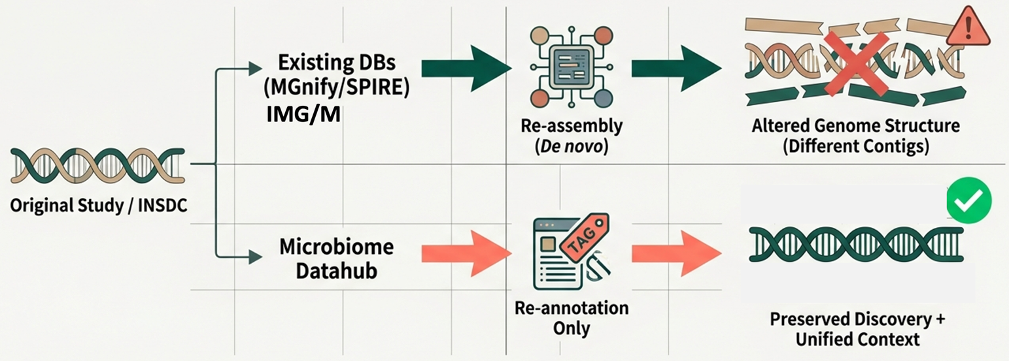
図: Microbiome Datahubと他の大規模MAGデータベースにおけるMAGの違い
●用語解説●
MAG:Metagenome Assembled Genomeの略称であり、メタゲノム配列をアセンブルして得られた長い配列(コンティグ)から、配列の連続塩基組成や配列の相対存在量等の情報をもとにコンティグをクラスタリング(binning)して得られる、仮想的なゲノム配列を指します。
詳しい研究内容について
メタゲノム由来ゲノムを収集・整理した統合データベース「Microbiome Datahub」を開発 ―21万ゲノム以上のMAG配列と環境・機能情報を統合し、微生物研究を加速― [PDF]
メタゲノム由来ゲノムを収集・整理した統合データベース「Microbiome Datahub」を開発 ―21万ゲノム以上のMAG配列と環境・機能情報を統合し、微生物研究を加速― [PDF]
研究領域情報
数理生物情報
数理生物情報
 京都大学 化学研究所
京都大学 化学研究所 国際共同利用・共同研究拠点
国際共同利用・共同研究拠点